Research Abstract
ゴムノキゲノムにはゴム生合成に関係する遺伝子ファミリーの増加が認められた
The rubber tree genome shows expansion of gene family associated with rubber biosynthesis
2016年6月24日 Scientific Reports 6 : 28594 doi: 10.1038/srep28594
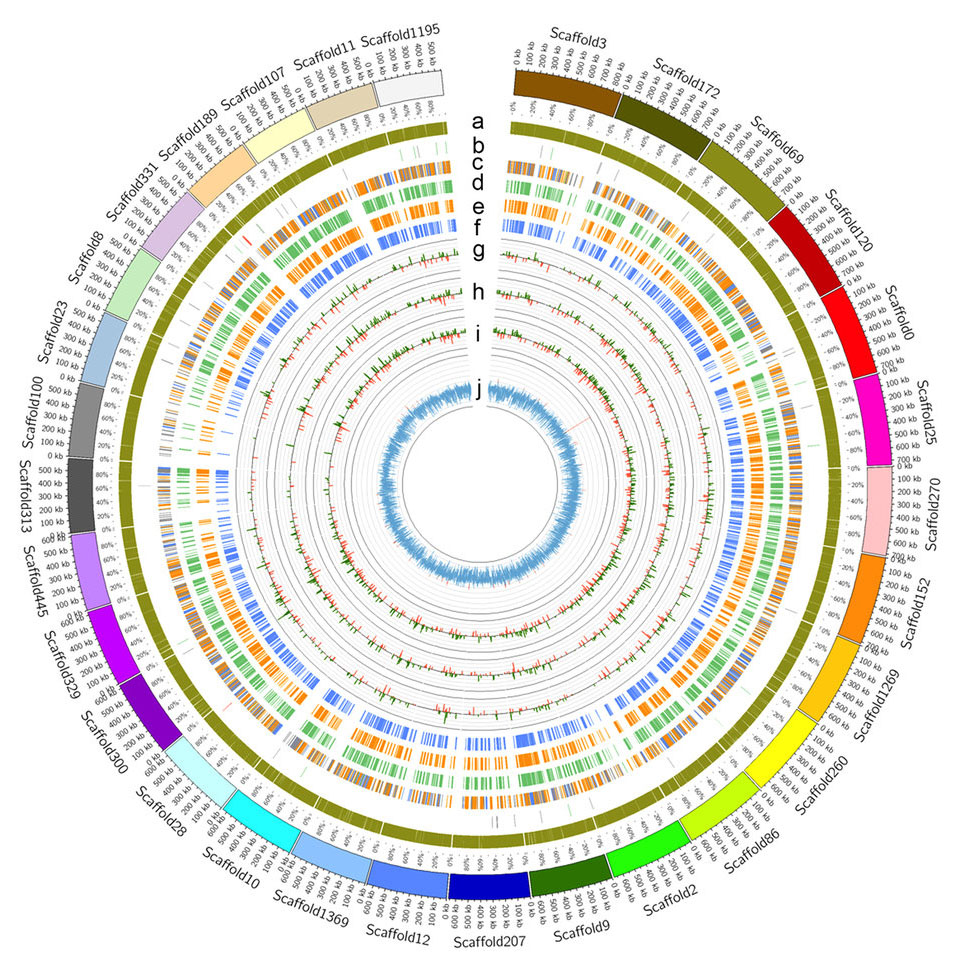
トウダイグサ科に属するパラゴムノキ(Hevea brasiliensis Muell. Arg)は、高品質天然ゴムの商業生産に利用されている唯一の天然資源である。多くの工業的用途に関して、天然ゴムのラテックスの特性は、合成品で代替することがほぼ不可能である。ゴムの高収率生合成の分子機序に関しては、情報がいまだに不足している。本論文では、広く栽培されているパラゴムノキクローンRRIM 600の網羅的全ゲノム解析の結果を示す。ゲノムのアセンブリーは、IlluminaおよびPacBioの配列データを組み合わせて約155倍のカバー率で行った。全長は1.55 Gbで、72.5%は反復DNA配列であった。タンパク質をコードすることが確実な遺伝子は、合計で8万4440個予測された。比較ゲノム解析の結果、パラゴムノキとほかのトウダイグサ科植物のゲノムには強いシンテニーが見いだされた。我々のデータは、高レベルのラテックスを生産するパラゴムノキの能力が、ゲノム内でのゴム生合成関連遺伝子の増加、およびそうした遺伝子のラテックス中での高発現によるものであることを示唆している。CAGE(cap analysis gene expression)法のデータを利用することにより、ゴム生合成関連遺伝子の組織特異的な転写プロファイルが示され、選択的な転写開始部位による転写調節の手段が明らかになった。本研究はパラゴムノキの生物学的理解を促進し、今後ゴムノキに関して農業関連の改良を行うための有用なゲノムリソースを提供するものである。
Corresponding Authors
Hevea brasiliensis Muell. Arg, a member of the family Euphorbiaceae, is the sole natural resource exploited for commercial production of high-quality natural rubber. The properties of natural rubber latex are almost irreplaceable by synthetic counterparts for many industrial applications. A paucity of knowledge on the molecular mechanisms of rubber biosynthesis in high yield traits still persists. Here we report the comprehensive genome-wide analysis of the widely planted H. brasiliensis clone, RRIM 600. The genome was assembled based on ~155-fold combined coverage with Illumina and PacBio sequence data and has a total length of 1.55 Gb with 72.5% comprising repetitive DNA sequences. A total of 84,440 high-confidence protein-coding genes were predicted. Comparative genomic analysis revealed strong synteny between H. brasiliensis and other Euphorbiaceae genomes. Our data suggest that H. brasiliensis’s capacity to produce high levels of latex can be attributed to the expansion of rubber biosynthesis-related genes in its genome and the high expression of these genes in latex. Using cap analysis gene expression data, we illustrate the tissue-specific transcription profiles of rubber biosynthesis-related genes, revealing alternative means of transcriptional regulation. Our study adds to the understanding of H. brasiliensis biology and provides valuable genomic resources for future agronomic-related improvement of the rubber tree.

