Research Abstract
次世代シーケンシングと無細胞ディスプレイ法の組み合わせにより、信頼性のあるインタラクトームデータをハイスループットに産出する
Next-generation sequencing coupled with a cell-free display technology for high-throughput production of reliable interactome data
2012年10月9日 Scientific Reports 2 : 691 doi: 10.1038/srep00691
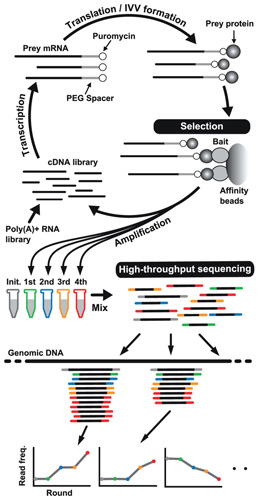
次世代シーケンシング技術(NGS)は、さまざまなオミックス研究に利用され、生物学や医学における多くの発見につながっている。しかし、シーケンシングによって検出されたタンパク質間インタラクトームのデータセットには、ハイスループットに得られたものがほとんどない。なぜなら、タンパク質間相互作用解析は、相互作用を調べるために多くの細胞操作を必要とするからである。また、ハイスループットデータの信頼性が低いことも課題である。本研究では、無細胞ディスプレイ法とNGSを組み合わせることで、インタラクトームデータセットの網羅性と信頼性の両方を改善できることを報告する。この完全な無細胞の方法は、ハイスループットかつ広い検出空間を提供することで、クローンを用いずにインタラクトームを調べることができる。また、NGSから得られた定量的情報により、偽陽性の数を効果的に削減できる。この方法はベイトタンパク質との相互作用だけでなく、DNAやRNA、そして化合物と相互作用するタンパク質のin vitroでの検出にも適している。このように、本手法はタンパク質配列の広い空間とインタラクトームのネットワークを探索するための、一般的な手法となるだろう。
藤森 茂雄1, 平井 直也1, 大橋 広行1, 増岡 和代1, 錦見 昭彦2, 福井 宣規2, 鷲尾 尊規1, 3, 押久保 朋宏1, 4, 山下 辰博1, 5 & 宮本 悦子1, 6
- 東京大学医科学研究所 インタラクトーム医科学社会連携研究部門
- 九州大学生体防御医学研究所 個体機能制御学部門 免疫遺伝学分野
- 株式会社 理研ジェネシス
- 株式会社 富士通アドバンストエンジニアリング
- 富士通株式会社 バイオIT事業開発本部
- 東京大学医科学研究所・ヒトゲノム解析センター
Next-generation sequencing (NGS) has been applied to various kinds of omics studies, resulting in many biological and medical discoveries. However, high-throughput protein-protein interactome datasets derived from detection by sequencing are scarce, because protein-protein interaction analysis requires many cell manipulations to examine the interactions. The low reliability of the high-throughput data is also a problem. Here, we describe a cell-free display technology combined with NGS that can improve both the coverage and reliability of interactome datasets. The completely cell-free method gives a high-throughput and a large detection space, testing the interactions without using clones. The quantitative information provided by NGS reduces the number of false positives. The method is suitable for the in vitro detection of proteins that interact not only with the bait protein, but also with DNA, RNA and chemical compounds. Thus, it could become a universal approach for exploring the large space of protein sequences and interactome networks.

