ゲノム塩基配列の比較により明らかになった乾燥無代謝休眠をするユスリカの極限乾燥耐性のゲノム的特徴
Comparative genome sequencing reveals genomic signature of extreme desiccation tolerance in the anhydrobiotic midge
2014年9月12日 Nature Communications 5 : 4784 doi: 10.1038/ncomms5784
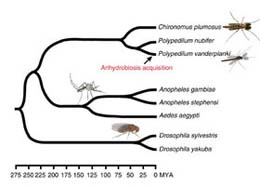
乾燥無代謝休眠とは、水が失われた状態に対する耐性適応の究極の例であり、生物が再び水に浸漬するまで無代謝状態で生存可能なことを指している。本論文は、乾燥無代謝休眠をする唯一の昆虫であるネムリユスリカ(Polypedilum vanderplanki)の幼虫に特異的に見られるような、極限乾燥耐性のゲノム的背景を調べた比較解析に関する初めての報告である。我々は、ネムリユスリカと、近縁種で乾燥感受性のヤモンユスリカ(p. nubifer)のゲノムを比較した。乾燥無代謝休眠をするネムリユスリカのゲノムには、この種に特異的な多コピーな遺伝子で構成されるクラスターが含まれていて、これらの遺伝子の産物が分子保護する役割を果たしていることが分かった。さらに、このゲノムには既知の保護タンパク質とよく似たタンパク質をコードする遺伝子のグループが複数含まれていた。しかし、このような遺伝子群はネムリユスリカのゲノム内で、この2種のユスリカや他の昆虫に共有されている各遺伝子の古典的オルソログの存在する場所とは異なった、別のパラログクラスター内に位置していた。これらのパラログクラスターの転写物は、乾燥した幼虫のmRNAプールの大半を占めており、乾燥無代謝休眠の決め手であることはほぼ確実である。2種のユスリカのオルソログ発現パターンの比較から、ネムリユスリカには乾燥特異的な遺伝子発現系が存在することの証拠が得られた。
Oleg Gusev1,2,3, 末次 克行1, Richard Cornette1, 川島 武士4, Maria D. Logacheva5,6,7, Alexey S. Kondrashov5,8, Aleksey A. Penin5,7,9, 畑中 理恵1, 菊田 真吾1, 志村 幸子1, 金森 裕之1, 片寄 裕一1, 松本 隆1, Elena Shagimardanova2, Dmitry Alexeev10, Vadim Govorun10, Jennifer Wisecaver11, Alexander Mikheyev4, 小柳 亮4, 藤江 学4, 西山 智明12, 重信 秀一13,14, 柴田 朋子13, Veronika Golygina15, 長谷部 光泰13,14, 奥田 隆1, 佐藤 矩行4 & 黄川田 隆洋1
- 農業生物資源研究所
- カザン大学(ロシア)
- 宇宙航空研究開発機構 宇宙科学研究所 ISS科学プロジェクト室
- 沖縄科学技術大学院大学
- モスクワ大学 生物情報工学(ロシア)
- モスクワ大学 A. N. ベロゼルスキー生物物理化学研究所(ロシア)
- ロシア科学アカデミー 情報伝送研究所(ロシア)
- ミシガン大学 生態進化生物学 生物学研究所(アメリカ)
- モスクワ大学 生物学部 遺伝学科(ロシア)
- ロシア連邦医療生物学庁 生物物理化学研究所(ロシア)
- ヴァンダービルト大学 生物学(アメリカ)
- 金沢大学 学際科学実験センター
- 基礎生物学研究所
- 総合研究大学院大学 生命科学研究科 基礎生物学専攻
- ロシア科学アカデミー 細胞学・遺伝学研究所(ロシア)

