等温増幅および携行可能な塩基配列解読装置を用いたデングウイルスの血清型判定
Serotyping dengue virus with isothermal amplification and a portable sequencer
2017年6月14日 Scientific Reports 7 : 3510 doi: 10.1038/s41598-017-03734-5
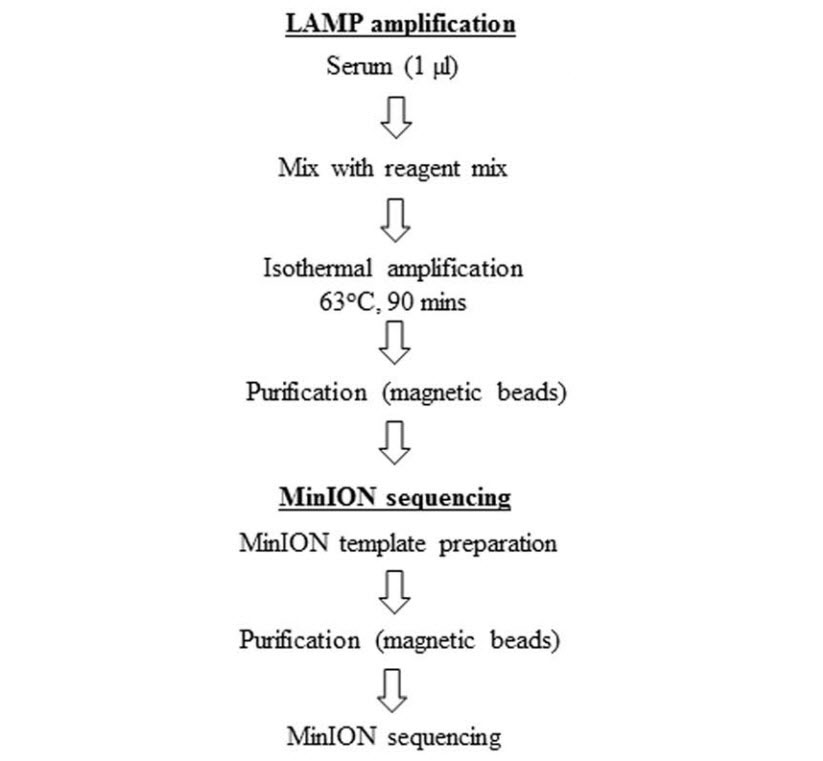
最近、ナノポア型の携行可能なDNA塩基配列解読装置が開発されたことにより、DNA塩基配列解読についての我々の考え方が変わってきている。試料を採取した現場で直接塩基配列解読を行うことができるのだ。本論文では、デング熱をモデルとして用い、熱帯病の病原体を検出および遺伝型判定する新しい方法を開発したことを報告する。塩基配列解読装置と水浴のみが必要な等温増幅とを組み合わせることで、標的とするウイルスゲノムを簡単に増幅および塩基配列解読することができた。血清試料から始めて、全行程を1日で完了できた。141人のインドネシア人患者から採取した血液試料の解析から、この方法を用いれば、高い感度と特異性でデングウイルスの臨床的同定と血清型判定を行うことができることが実証された。総検出成功率は79%で、合計58個のSNVが検出された。80人のベトナム人と12人のタイ人の試料についても同様の解析を行うと、同様の性能が示された。我々は、得られた塩基配列情報を基盤として、この手法により、病原体の年間あるいは地域的な多様化が病因となるかどうかを解析するための不可欠な情報を得られることを示している。
Corresponding Author
The recent development of a nanopore-type portable DNA sequencer has changed the way we think about DNA sequencing. We can perform sequencing directly in the field, where we collect the samples. Here, we report the development of a novel method to detect and genotype tropical disease pathogens, using dengue fever as a model. By combining the sequencer with isothermal amplification that only requires a water bath, we were able to amplify and sequence target viral genomes with ease. Starting from a serum sample, the entire procedure could be finished in a single day. The analysis of blood samples collected from 141 Indonesian patients demonstrated that this method enables the clinical identification and serotyping of the dengue virus with high sensitivity and specificity. The overall successful detection rate was 79%, and a total of 58 SNVs were detected. Similar analyses were conducted on 80 Vietnamese and 12 Thai samples with similar performance. Based on the obtained sequence information, we demonstrated that this approach is able to produce indispensable information for etiologically analyzing annual or regional diversifications of the pathogens.

